
Nina Pastor
@ninapastor6
Biomedical scientist with a soft spot for biophysics. Useless with a pipette, at home with a computer and lots of coffee. I live and breathe molecules.
ID: 1295503689625538564
http://www.cidc.uaem.mx 17-08-2020 23:32:33
196 Tweet
61 Followers
74 Following

It's here again! check out the 3rd Building Bridges in #computational #biophysics ! Register using their QR code Biophysical Society







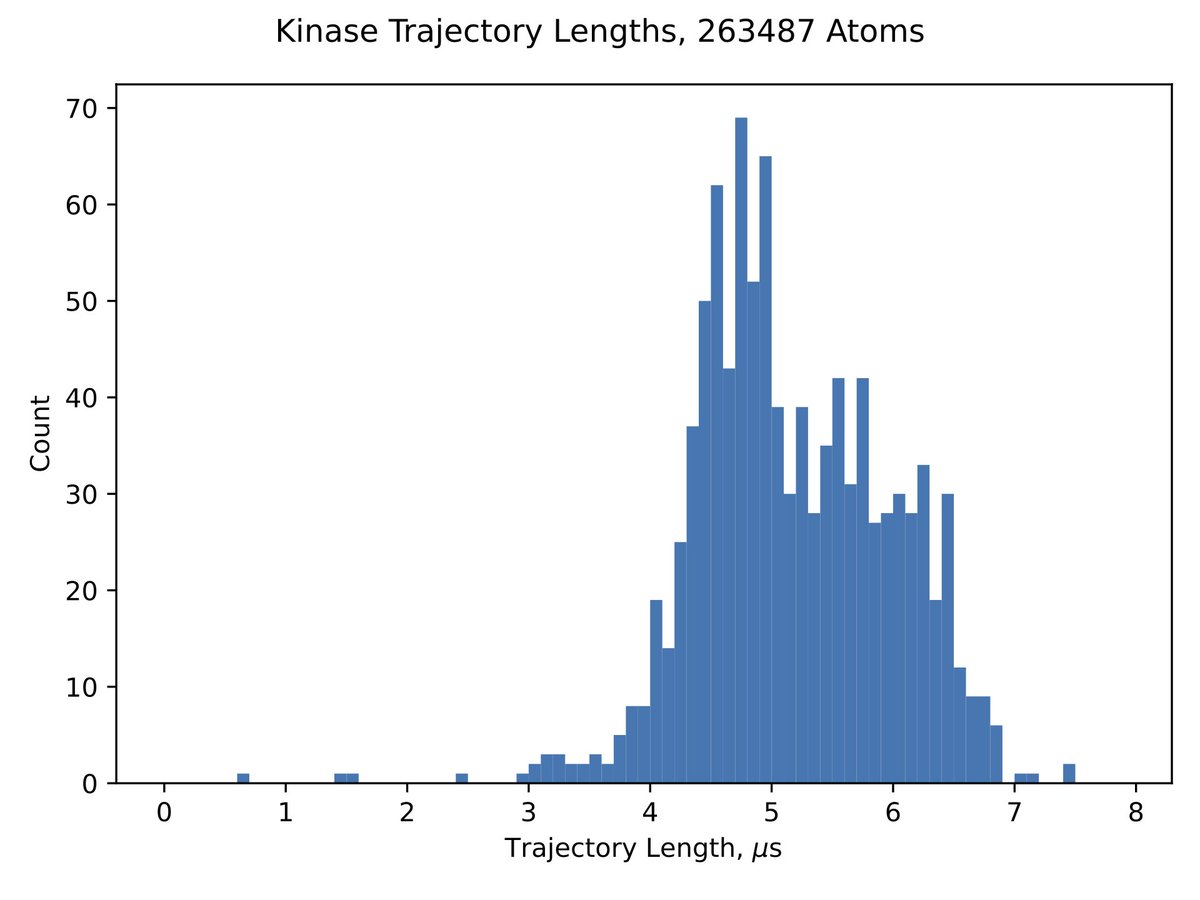
Its amazing how much data we have to work with thanks to Folding@home. In this project, we have 1,000 simulations that are each 5 microseconds long on average, for an aggregate of over 5 milliseconds of data! #compchem See sim length histogram



Hi LatinXChem, Nina Pastor and I are presenting our work: ‘Flexibility and self-inhibition: Exploring the conformational landscape of Cre recombinase’ at #LatinXChem24 #LatinXChemBio #Bio19 #Biophysics #MolecularDynamics #CreRecombinase



¡hola a todo mundo! los invito a este curso introductorio de modelado de estructuras de proteínas. Lo único que necesitan es una computadora a la cual le puedan instalar el visualizador gratuito VMD. Son 30 horas interactivas. para informes, por favor escríbanme ([email protected])


Very happy to share our next extension to the CALVADOS protein force field: If you want to explore the changes in global dimensions of a disordered protein upon phosphorylation: give it a read and a try! Big thank you to Giulio Tesei , Kresten Lindorff-Larsen and Gustav Hedemark



